A promoção de crescimento vegetal mediada por microrganismos (MPCV) constitui um eixo estratégico da bioeconomia e da agricultura. Este trabalho propõe uma abordagem integrada de cienciometria e genômica comparativa aplicadas ao gênero Nitrospirillum, um gênero de bactérias diazotróficas promotoras de crescimento vegetal. A análise cienciométrica (2022–2025), conduzida na base Web of Science e visualizada no VOSviewer, revelou a concentração de estudos em poucos gêneros microbianos, evidenciando a subexploração de táxons alternativos. Para aprofundar essa lacuna, foi desenvolvido um dicionário funcional contendo 60 termos distribuídos em 19 categorias de mecanismos de promoção de crescimento, processado no RStudio. Paralelamente, um pipeline genômico foi aplicado na plataforma BV-BRC para mapear genes codificantes desses mecanismos em genomas de Nitrospirillum, possibilitando comparar seu potencial biotecnológico com o de gêneros mais estudados. Apesar do uso consolidado de Nitrospirillum em formulações comerciais aplicadas à cultura da cana-de-açúcar, o conhecimento sobre sua base genômica e seu potencial de aplicação em novas culturas ainda é incipiente, representando uma oportunidade estratégica para inovação em bioinsumos. Os resultados indicam que Nitrospirillum apresenta um repertório genético equivalente em diferentes funções-chave e evidencia rotas alternativas de biossíntese auxínica, sugerindo estratégias metabólicas diferenciadas de promoção do crescimento vegetal. A integração das abordagens cienciométrica e genômica demonstra como ferramentas bioinformáticas podem direcionar estratégias de prospecção microbiana e fortalecer a autonomia tecnológica nacional.
Autores: Francisco Matheus Medeiros de Freitas, Alberto Fernandes de Oliveira Junior, Marcia Soares Vidal, Jerri Édson Zilli
Introdução
Microrganismos Promotores de Crescimento Vegetal (MPCV) contribuem para a sustentabilidade agrícola (Figura 1) ao reduzir o uso de fertilizantes químicos e promover resiliência vegetal [1].


Apesar disso, grande parte das pesquisas concentra-se em poucos gêneros bem estabelecidos gêneros como Bacillus e Pseudomonas, limitando a exploração da diversidade microbiana disponível [2] (Figura 2). Esse padrão ocorre porque os estudos tendem a privilegiar organismos-modelo já consolidados, o que reduz a atenção destinada a grupos menos investigados, embora ecologicamente abundantes e funcionalmente relevantes. Esse viés restringe a descoberta de novas funções e interações microbianas essenciais para ampliar o potencial biotecnológico do solo [3].
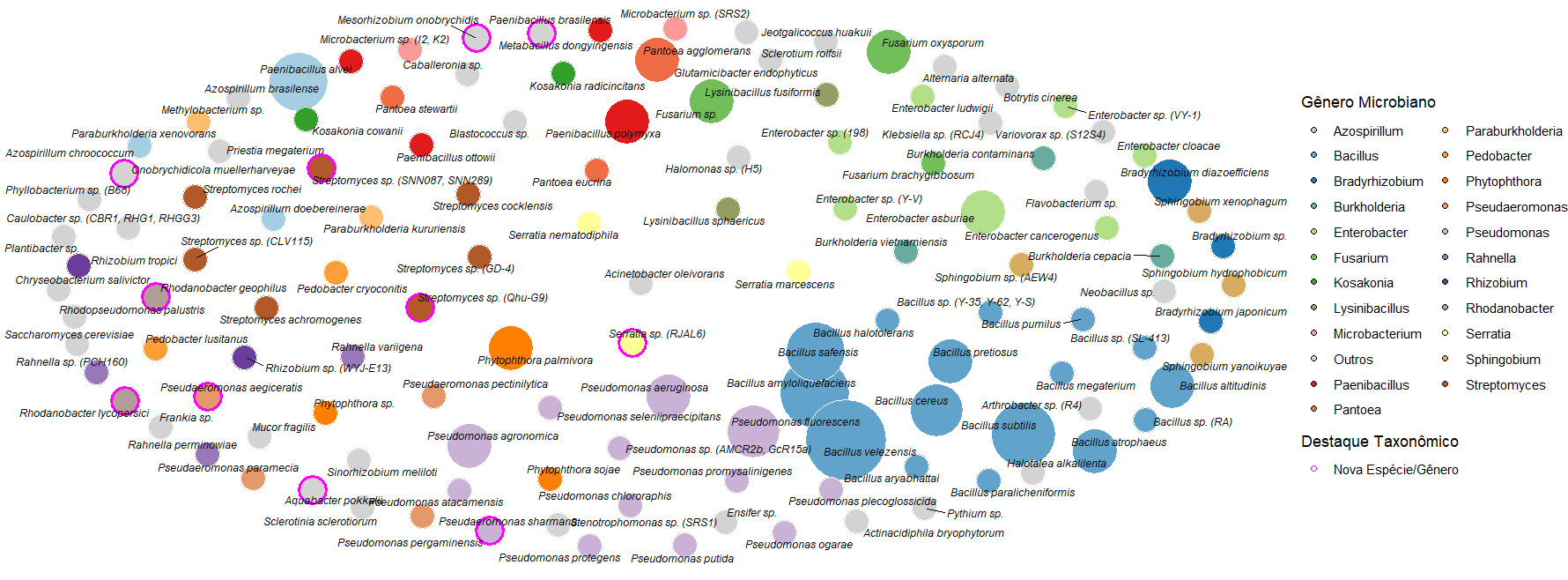

Este cenário contrasta com o de gêneros como Nitrospirillum, que possui uso comercial consolidado como inoculante para cana-de-açúcar no Brasil [4], mas permanece sub-representado na literatura recente. O gênero Nitrospirillum, formalmente proposto em 2014 [5], expandiu-se com a descrição de Nitrospirillum viridazoti sp. nov. [6], isolada de gramíneas brasileiras. Estudos recentes ampliaram substancialmente o número de táxons propostos, com registros adicionais em hospedeiros não gramíneos e a recente formalização de seis novas espécies [7]. Apesar do potencial, os mecanismos moleculares de interação com plantas necessitam de melhor caracterização.
Para compreender melhor esse cenário, utilizou-se uma estratégia integrada combinando cienciometria e genômica comparativa. A hipótese central é que a aplicação de ferramentas bioinformáticas pode revelar oportunidades tecnológicas negligenciadas, acelerando o desenvolvimento de insumos microbianos mais diversificados e adaptados às condições tropicais.
Métodos e abordagens utilizadas
Diagnóstico Cienciométrico
Para quantificar a distribuição taxonômica nas pesquisas com MPCV, foi realizada análise cienciométrica na Web of Science (2022-2025), resultando em 166 artigos após critérios de elegibilidade (Figura 3). A análise de co-ocorrência de palavras-chave foi conduzida no VOSviewer (versão 1.6.20) [8], mapeando a estrutura intelectual do campo.


Figura 3. Fluxograma da estratégia de busca, seleção de artigos e tratamento de dados. Fonte: Elaborado pelo autor, 2025.
O processamento computacional foi realizado no RStudio (versão 2025.09.1-401) utilizando os pacotes tidyverse, readxl, stringr, ggplot2 e viridis. Foi desenvolvido sistema de mineração de texto que combinou: (i) busca direta por 30 gêneros bacterianos previamente conhecidos; e (ii) identificação não supervisionada de gêneros emergentes através de padrões de expressão regular, permitindo censo taxonômico abrangente.
Para caracterização funcional, foi criado um dicionário taxonômico com 60 termos específicos organizados em 19 categorias funcionais, abrangendo mecanismos nutricionais, produção de fitormônios, biocontrole, tolerância a estresses e adaptações ecológicas. O processo incluiu consolidação textual, busca por padrões adaptativos, contagem quantitativa e classificação por intensidade, com validação através de amostragem aleatória.
Análise Genômica Comparativa
Para caracterização do potencial biotecnológico de Nitrospirillum, foi aplicada análise comparativa na plataforma BV-BRC (Bacterial and Viral Bioinformatics Resource Center) [9] utilizando genomas anotados disponíveis. A estratégia incluiu: (i) seleção e agrupamento de genomas de estirpes tipo; (ii) caracterização filogenômica via ferramenta CodonTree com Azospirillum brasiliense como referência; (iii) análise comparativa global de identidades proteicas empregando “Protein Comparison”; e (iv) mapeamento sistemático de genes-alvo através de heatmaps metabólicos e ferramentas de “Comparative Systems”.
A abordagem incluiu controles positivos e comparações com gêneros estabelecidos para validação metodológica, investigando vias relacionadas à biossíntese de auxinas, produção de exopolissacarídeos, solubilização de nutrientes e atividade de ACC-deaminase.
Conclusão
A abordagem integrada de cienciometria e genômica comparativa demonstrou ser uma estratégia eficiente para identificar e caracterizar recursos microbianos com potencial biotecnológico. A metodologia desenvolvida permitiu diagnosticar a concentração de pesquisas em poucos gêneros bacterianos e estabelecer as bases para a exploração sistemática do gênero Nitrospirillum. Esses resultados representam uma contribuição concreta para a diversificação de insumos biológicos e para o fortalecimento da bioeconomia, alinhando-se aos Objetivos de Desenvolvimento Sustentável, especialmente à agricultura sustentável (ODS 2), à promoção da inovação (ODS 9) e à valorização da biodiversidade (ODS 15).
A aplicação de ferramentas bioinformáticas mostrou-se promissora para direcionar investigações futuras, acelerar o desenvolvimento de soluções biotecnológicas mais eficientes e ambientalmente responsáveis, ampliando as possibilidades de uso do patrimônio microbiano brasileiro.
Agradecimentos. O presente trabalho foi realizado com apoio do INCT MicroAgro: “Inovações biotecnológicas com microrganismos para uma agricultura produtiva e sustentável” (CNPq 408267/2024, Fundação Araucária); a Fundação Carlos Chagas Filho de Amparo à Pesquisa do Estado do Rio de Janeiro (FAPERJ), processo SEI-260003/005221/2025, e por meio dos projetos E-26/201.074/2022 e E-26/210.303/2021; e apoio adicional do CNPq (Processo 405968/2022-1).
Referências
[1] Backer, R.; Rokem, J. S.; Ilangumaran, G.; Lamont, J.; Praslickova, D.; Ricci, E.; Subramanian, S.; Smith, D. L. Plant growth-promoting rhizobacteria: Context, mechanisms, and roadmap to commercialization of biostimulants for sustainable agriculture. Frontiers in Plant Science, 9:1473. (2018). DOI: 10.3389/fpls.2018.01473.
[2] Bashan, Y.; de-Bashan, L. E.; Prabhu, S. R.; Hernández, J.-P. Advances in plant growth-promoting bacterial inoculant technology: formulations and practical perspectives (1998-2013). Plant and Soil, 378:1-33. (2014). DOI: 10.1007/s11104-013-1956-x.
[3] Berg, G.; Rybakova, D.; Fischer, D.; Cernava, T.; Champomier-Vergès, M.-C.; Charles, T.; Chen, X.; Cocolin, L.; Eversole, K.; et al. Microbiome definition re-visited: old concepts and new challenges. Microbiome, 8:103. (2020). DOI: 10.1186/s40168-020-00875-0.
[4] Schwab, S.; Pires, A. S.; Candido, G. Z.; Saggin Júnior, O. J.; Reis, V. M.; Cruz, L. M. Analysis of the endophytic microbiota of roots and culms of two commercial sugarcane cultivars inoculated with a synthetic microbial community. Applied Soil Ecology, 195:105235.(2024). DOI: 10.1016/j.apsoil.2023.105235.
[5] Lin, S.-Y.; Hameed, A.; Shen, F.-T.; Liu, Y.-C.; Hsu, Y.-H.; Shahina, M.; Lai, W.-A.; Young, C.-C. Description of Niveispirillum fermenti gen. nov., sp. nov., isolated from a fermentor in Taiwan; transfer of Azospirillum irakense (1989) as N. irakense comb. nov.; and reclassification of A. amazonense (1983) as Nitrospirillum amazonense gen. nov. Antonie van Leeuwenhoek, 105:1149–1162. (2014). DOI: 10.1007/s10482-014-0176-6.
[6] Baldani, J.I.; Dos Santos Ferreira, N.; Schwab, S.; Reis, V.M.; de Barros Soares, L.H.; Simões-Araujo, J.L.; Dos Santos Dourado, F.; Bach, E.; Camacho, N.N.; de Oliveira, A.M.; et al. Nitrospirillum viridazoti sp. nov., an efficient nitrogen-fixing species isolated from grasses. Current Microbiology, 81:144. (2024). DOI: 10.1007/s00284-024-03665-1.
[7] Zilli, J. E., Schwab, S.; Ferreira, N. D. S., Reis, V. M., Oliveira Júnior, A. F., Simões-Araujo, J. L., Soares, L. H. B., Dourado, F. D. S., Bach, E., Roesch, L. F. W., Rossi, C. N., Lima de Souza, K. M., Alves, B. J. R., Silva, A. L., Baldani, J. I.. (2025). Diversity of grass-associated Nitrospirillum and proposal of six novel species. Brazilian Journal of Microbiology. DOI: 10.1007/s42770-025-01802-x.
[8] van Eck, N.J., Waltman, L. Software survey: VOSviewer, a computer program for bibliometric mapping. Scientometrics 84:523-538. (2010). DOI: 10.1007/s11192-009-0146-3.
[9] Olson, R. D.; Assaf, R.; Brettin, T.; Conrad, N.; Cucinell, C.; Davis, J. J.; Dempsey, D. M.; Dickerman, A.; Dietrich, E. M.; Kenyon, R. W.; Kuscuoglu, M.; Lefkowitz, E. J.; Lu, J.; Machi, D.; Macken, C.; Mao, C.; Niewiadomska, A.; Nguyen, M.; Olsen, G. J.; Overbeek, J. C.; Parrello, B.; Parrello, V.; Porter, J. S.; Pusch, G. D.; Shukla, M.; Singh, I.; Stewart, L.; Tan, G.; Thomas, C.; VanOeffelen, M.; Vonstein, V.; Wallace, Z. S.; Warren, A. S.; Wattam, A. R.; Xia, F.; Yoo, H.; Zhang, Y.; Zmasek, C. M.; Scheuermann, R. H.; Stevens, R. L.. Introducing the Bacterial and Viral Bioinformatics Resource Center (BV-BRC): a resource combining PATRIC, IRD and ViPR. Nucleic Acids Research, 51(D1): D678–D689. (2023). DOI: 10.1093/nar/gkac1003.


